Jenseits der Netzhaut: Maschinelle Lernmodelle zur photochemischen Steuerung von Rhodopsinen
Hector RCD Awardee Prof. Dr. Carolin Müller
Hector Fellow Prof. Dr. Klaus Robert Müller
Hector Fellow Prof. Dr. Peter Hegemann
Das Projekt entwickelt ein Machine‑Learning‑Framework zur genauen Vorhersage angeregter Zustände von Rhodopsinen. Dafür wird ein Datensatz aus quantenchemischen Berechnungen an Retinal‑Derivaten in proteinähnlichen Umgebungen erstellt und zum Modelltraining verwendet. Durch wiederholte Synthese und spektroskopische Analyse gezielt entworfener Rhodopsin‑Varianten werden die Modelle iterativ geprüft und verbessert. Die trainierten Modelle zeigen, wie die Proteinmatrix die Reaktivität des Chromophors und sein Spektrum beeinflusst, und erlauben schnelle, präzise Abschätzungen von Spektren und photochemischen Reaktionswegen. Ziel ist eine datengetriebene Plattform für das rationale Design lichtempfindlicher Proteine und die beschleunigte Entwicklung neuer Photorezeptoren. Beteiligt an diesem Projekt sind Hector RCD Awardee Prof. Dr. Carolin Müller, Hector Fellow Prof. Dr. Klaus Robert Müller und Hector Fellow Prof. Dr. Peter Hegemann.
Rhodopsinen sind lichtempfindliche Proteine, die ein kovalent gebundenes Retinal‑Chromophor als fotoaktive Einheit besitzen. Obwohl alle Rhodopsine diesen gemeinsamen Kern teilen, zeigen sie ein breites Spektrum photochemischer Reaktionen – von einfachen E/Z‑Isomerisationen bis zu mehrstufigen Pfaden – und damit unterschiedliche Funktionen. Diese Vielfalt entsteht aus dem feinen Zusammenspiel zwischen der intrinsischen Reaktivität des Chromophors und der modulierenden Wirkung der umgebenden Proteinmatrix auf den Dunkel‑, den angeregten und den photoproduct‑Zustand.
Ein tiefes Verständnis dieser Wechselwirkungen ist Voraussetzung, um die molekularen Prinzipien biologischer Lichtwahrnehmung zu entschlüsseln und die photochemische Reaktivität gezielt zu steuern. Experimentelle Methoden wie zeitaufgelöste UV/Vis‑ und Raman‑Spektroskopie liefern wertvolle Daten, doch die ultrafast‑dynamischen Prozesse erschweren deren Interpretation und führen häufig zu spekulativen Struktur‑Eigenschafts‑Beziehungen. Quantentheoretische Simulationen des angeregten Zustands bieten mechanistische Einblicke, sind jedoch für die großen Chromophor‑Protein‑Komplexe von Rhodopsinen praktisch unzugänglich.
Das Vorhaben adressiert diese Limitation, indem ein maschinelles‑Lern‑Framework (ML) entwickelt wird, das angeregte Zustände in kovalent gebundenen Systemen beschreibt und Rhodopsinen als Modell nutzt. Das Projekt vereint die Kompetenzen von Prof. Dr. Klaus Robert Müller (Maschinelles Lernen für Chemie und Physik), Prof. Dr. Carolin Müller (hochwertige QM/MM‑Daten und Erweiterung von ML‑Modellen für angeregte Zustände) und Prof. Dr. Peter Hegemann (synthetische, exprimierte und spektroskopisch untersuchte Rhodopsin‑Derivate). Durch die Kombination von massenselektiver Ion‑Soft‑Landing und ESR‑STM entsteht ein noch nicht vorhandener methodischer Durchbruch, der eine modulare Plattform für den kontrollierten Aufbau beliebiger molekularer Bausteine und deren Spin‑Kopplung bereitstellt und sich nahtlos auf größere Biomoleküle (z. B. Metall‑Proteine) übertragen lässt. Langfristig wird ein offenes Werkzeug‑Set für die Gemeinschaft geschaffen, das elementare Oberflächenphysik mit Quanten‑Information und Sensorik verknüpft und die Basis für die nächste Generation molekularer Quantensimulatoren und optogenetischer Werkzeuge legt.
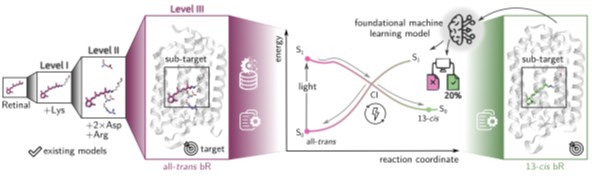
Abbildung 2: Illustration des übergeordneten Projektziels: Entwicklung von Machine‑Learning‑Modellen für angeregte Zustände, um über Retinal‑Modellsysteme (links) hinauszugehen und fotoinduzierte Phänomene des Retinals in seiner nativen Protein‑Umgebung (farbige Kästchen) vorherzusagen. Dies wird durch die Kombination von computergestützter Chemie, Machine Learning und Spektroskopie zur Etablierung eines grundlegenden ML‑Frameworks angegangen.
Betreut durch

Carolin Müller
Chemie, Informatik

Klaus-Robert Müller
Informatik, Mathematik & PhysikHector Fellow seit 2023

Peter Hegemann
Biologie, Chemie & MedizinHector Fellow seit 2015